瞬态和长期中断后肠道微生物的抗生素
万亿人类健康肠道微生物的援助,包括母乳的消化、分解纤维,帮助控制免疫系统。然而,抗生素治疗是已知干扰这些微生物的群落结构——500年至1000年细菌种类主要有有益的影响。
伯明翰阿拉巴马大学的研究现在已经跟踪干扰的水平应变的微生物取代另一个应变相同的物种在30个人都年轻,健康的成年人将有稳定的微生物群落。
”从我们的分析显示,复苏的能力对新病毒的数量和稳定是特定为每个单独的,”凯西莫罗说,博士领导的研究小组,在阿拉巴马大学名誉教授的细胞,发育生物学和整合。
复苏有潜在的健康影响的差异,明天说。
”有可能是作为个体的年龄,与每一个不同的数字和周期的抗生素治疗,微生物菌株的水库枯竭,导致自身内在复苏模式特定的微生物菌株,”他说。“理解这次复苏pattern-including特定菌株的出现抗生素可能是一个重要的长期的健康考虑。”
“在未来,这些细化的描述复苏模式也可以用来预测对内源性和外源性微生物病原体的易感性。”
UAB研究使用生物信息学工具来分析先前描述的研究18人被赋予一个抗生素,cefprozil,一周。他们收集粪便样本预处理,年底的抗生素治疗,在治疗后的三个月。UAB研究还分析了先前描述的数据12个人有三antibiotics-meropenem、庆大霉素和vancomycin-for四天。他们的粪便样本收集预处理;在治疗结束;四、38和治疗后的176天。6控制人没有接受抗生素也进行了分析。
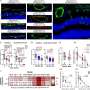
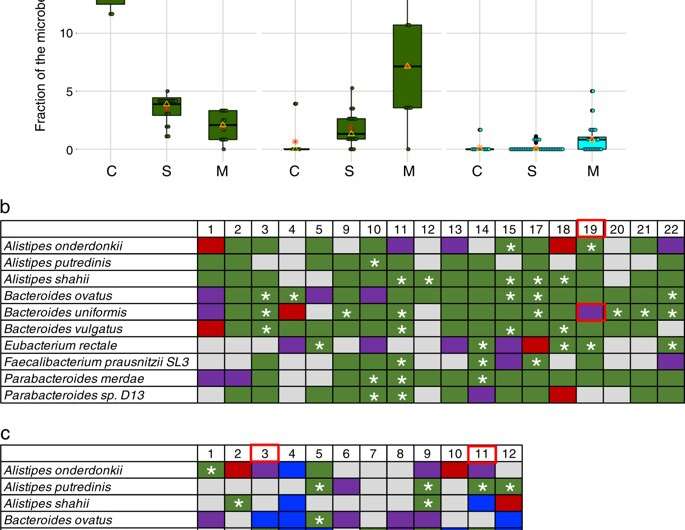
UAB的研究人员发现,一般来说,菌株的10个最丰富的物种保持稳定控制。在单个抗生素治疗18个人,15个人有瞬态新菌株后处理,反过来,取而代之的是原始菌株通过治疗后三个月。
相比之下,新菌株的三重个人有显著提高,坚持只要6个月治疗后,相比单一抗生素和个人控制。此外,瞬变压力的比例也明显高于多种抗生素的个人。这提出了一个长期的变化到另一种稳定的微生物状态,明天说。这些变化并不是由于经济增长率的差异。
“考虑到微生物的重要性人类健康与这些数据集,我们认为我们的结果可以用来帮助评估微生物稳定性在不同条件下,“明天说。“例如,我们现在可以指导临床调查人员判断某些治疗疾病的影响,如癌症和糖尿病,对肠道微生物群落可以显著的评估结果。此外,这种方法可以应用到病人的预处理和出院后识别那些可能需要进一步管理他们的微生物。”
“这项研究使用之前由UAB strain-tracking生物信息学工具,称为窗口相似Single-nucleotide-variant,或WSS,跟踪个人的微生物菌株从预处理抗生素治疗,”Hyunmin Koo说,博士,阿拉巴马大学的遗传学和Heflin基因组科学中心的信息分析。“这种技术进步分析抗生素的影响在人类肠道微生物群。微生物的先前的研究已经能够确定一个总体分类概要文件包括每个物种的相对多度信息,但显示限制在应变级别来区分每个物种或跟踪相同的应变在每个单独的纵向水平。
2017年,UAB研究人员使用WSS显示首次直接证明粪便捐赠microbes-used梭状芽胞杆菌治疗复发性感染人数在接受者粪便移植后数月或数年。
抗生素的研究发表在npj生物膜和微生物。
更多信息:Hyunmin古永锵et al .个性化恢复肠道微生物菌株的抗生素,npj生物膜和微生物(2019)。DOI: 10.1038 / s41522 - 019 - 0103 - 8