研究人员发现风险更低的方法来监测乳腺癌进展
安舒茨医学校园科罗拉多大学的研究人员已经发现了如何提取关键信息乳腺癌肿瘤和疾病进展通过分析血浆而不是使用更多侵入性组织切片。
说:“这只是一个抽血,这项研究的资深作者彼得•Kabos医学博士,医学副教授在医学肿瘤学部门在科罗拉多大学医学院和铜癌症中心成员。“这让我们看看表面下的定义特征的疾病。的优势在于,我们不需要做组织切片的重复。”
这项研究发表在《华尔街日报》科学的进步。
研究人员和临床医生分析等离子体定义的基因突变癌症。等离子体中的DNA包含更多的信息。
“我们只需要知道在哪里看,“Kabos说。
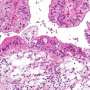
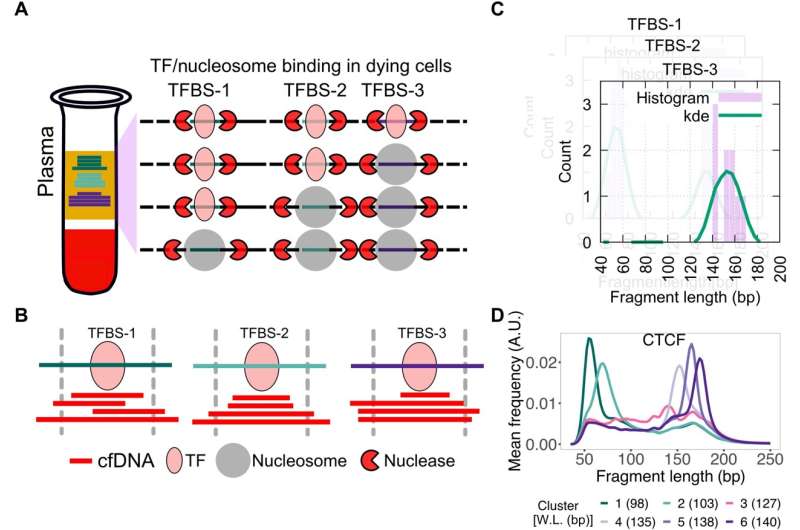
研究发现,血浆游离DNA (cfDNA)包含高分辨率、全基因组结合雌激素受体(ER)和FOXA1配置文件乳腺癌。FOXA1基因与乳腺癌有关。
“我们可以获得相同的分子信息直接从血液从组织切片,”说,这项研究的合著者其他高级斯拉马钱德兰,博士,生物化学和助理教授分子遗传学在铜医学院。“如果我们能提取这种信息没有做活检,我们可能对治疗决策提供更多的信息。”
死亡的细胞人体他们的内容释放到血液中,研究人员说。当癌症存在时,也会释放的碎片cfDNA为等离子体。
“这说明cfDNA有可能实时地图肿瘤表观基因组,因此可以帮助发现癌症从等离子体的监管环境,”拉玛钱德朗说。
根据研究,这些发现可能导致全基因组地图定义疾病状态,预测治疗效果和可能选择最有效的癌症治疗。不是实际的现在由于获得肿瘤组织所涉及的风险。
“在我们的研究中,我们利用另一种方法来获取相同的信息…以微创的方式来定义潜在疾病生物学、“Kabos和拉马钱德兰写道。
都说癌症的DNA上收集到的信息可以用来开发新的疗法。和相同的等离子体分析用于乳腺癌,他们说,可能与其他恶性肿瘤。
“鉴于大多数肿瘤释放cfDNA,相信我们的描述使用cfDNA ER +乳房肿瘤转录因子脚印代表肿瘤表型特征的冰山一角等离子体拉马钱德兰表示:“和适用于疾病,铜癌症中心成员。
进一步探索